This is the Linux app named sRNAWorkbench whose latest release can be downloaded as UEA_Workbench_4.7_update.zip. It can be run online in the free hosting provider OnWorks for workstations.
Download and run online this app named sRNAWorkbench with OnWorks for free.
Follow these instructions in order to run this app:
- 1. Downloaded this application in your PC.
- 2. Enter in our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 3. Upload this application in such filemanager.
- 4. Start the OnWorks Linux online or Windows online emulator or MACOS online emulator from this website.
- 5. From the OnWorks Linux OS you have just started, goto our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 6. Download the application, install it and run it.
SCREENSHOTS
Ad
sRNAWorkbench
DESCRIPTION
A suite of tools for analysing small RNA (sRNA) data from Next Generation Sequencing devices. Including expression profiling of known mirco RNA (miRNA), identification of novel miRNA in deep-sequencing data and identification of other interesting landmarks within high-throughput genetic data
Features
- Adaptor Remover: removes adaptor fragments from raw short read sequence data and outputs data to FASTA format.
- Filter: produces a filtered version of an sRNA dataset, controlled by several user-defined criteria, including sequence length, abundance, complexity, transfer and ribosomal RNA removal.
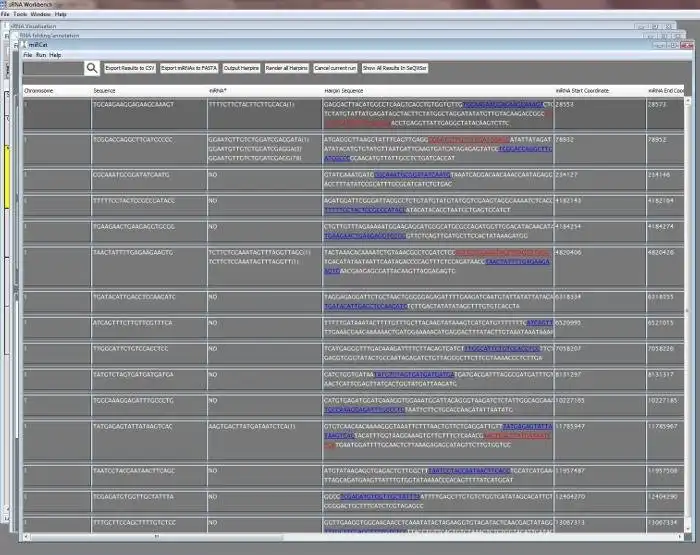
- miRCat2 (miRNA Categorisation): predicts mature miRNAs and their precursors from an sRNA dataset and a genome.
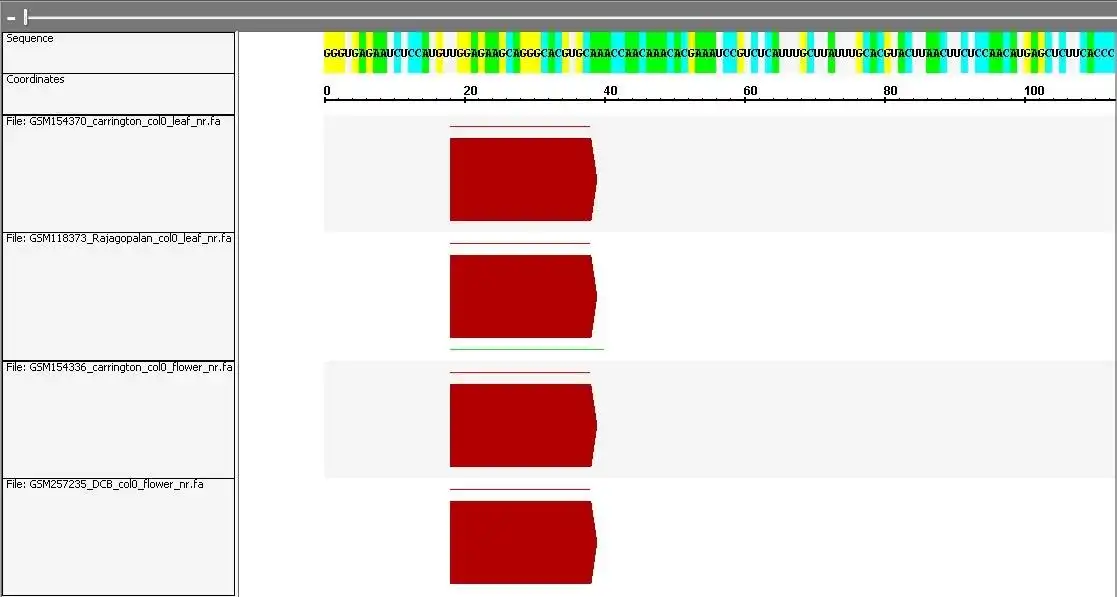
- SiLoCo (Short interfering RNA Locus Comparison): compares sRNA expression levels in multiple samples by grouping sRNAs into loci based on genomic location
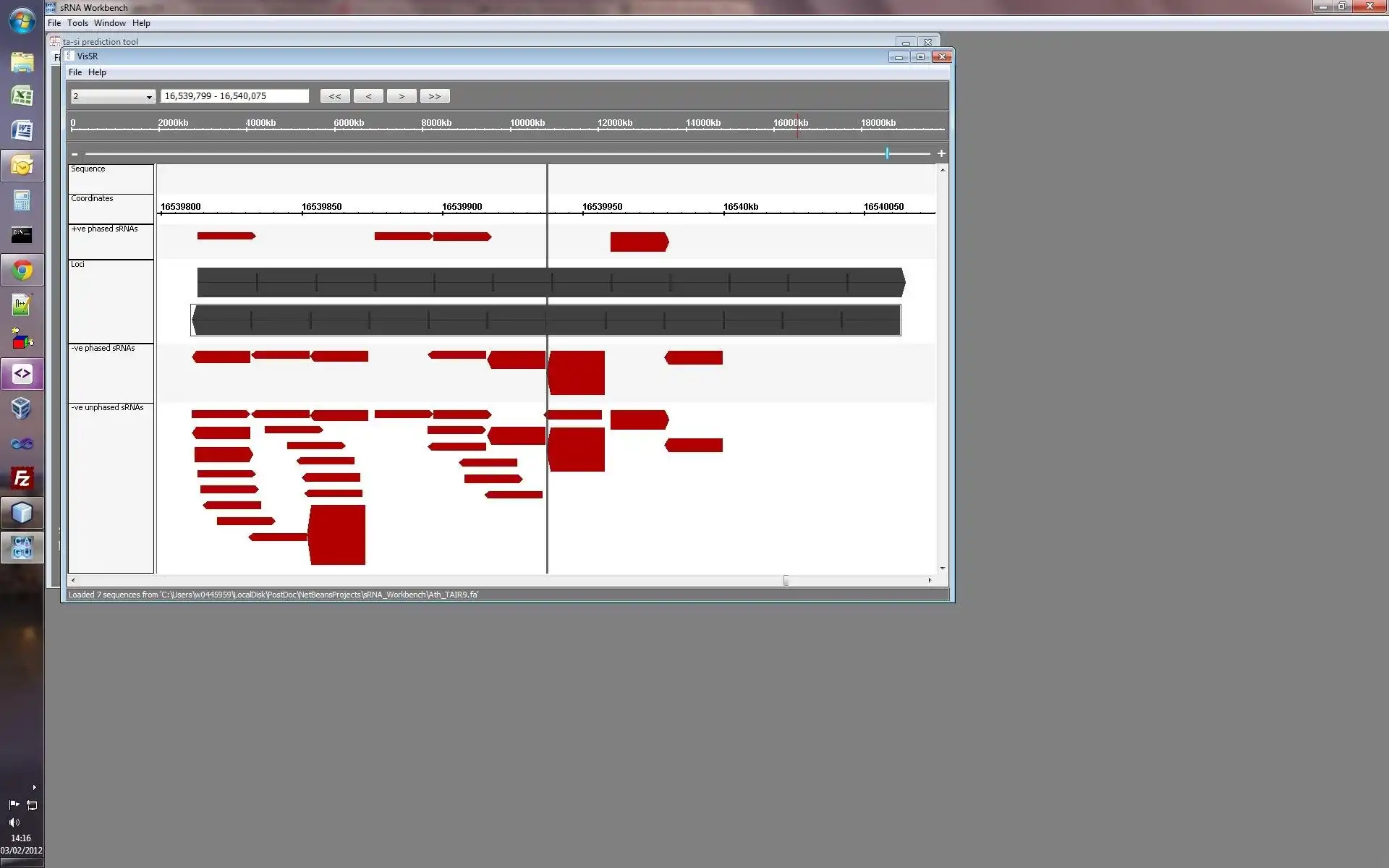
- ta-siRNA (trans-acting short interfering RNA): prediction of phased ta-siRNAs in plant sRNA datasets.
- miRProf (miRNA Profiler): determines normalised expression levels of sRNAs matching known miRNAs in miRBase.
- Hairpin Annotation: generates a secondary structure from an RNA sequence and highlights regions of interest using RNAplot
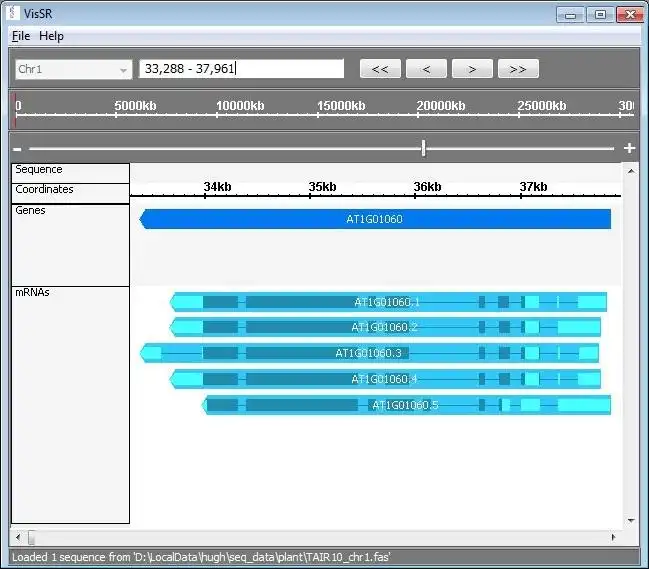
- VisSR (Visualisation of sRNAs): generate a visual representation of sRNAs and user-imported genomic features.
- PAREsnip2: Identify miRNA targets evidenced through the degradome
Audience
Science/Research
User interface
Java Swing
Programming Language
C++, Java
Categories
This is an application that can also be fetched from https://sourceforge.net/projects/srnaworkbench/. It has been hosted in OnWorks in order to be run online in an easiest way from one of our free Operative Systems.