This is the Linux app named Javamony to run in Linux online whose latest release can be downloaded as Javamony.jar. It can be run online in the free hosting provider OnWorks for workstations.
Download and run online this app named Javamony to run in Linux online with OnWorks for free.
Follow these instructions in order to run this app:
- 1. Downloaded this application in your PC.
- 2. Enter in our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 3. Upload this application in such filemanager.
- 4. Start the OnWorks Linux online or Windows online emulator or MACOS online emulator from this website.
- 5. From the OnWorks Linux OS you have just started, goto our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 6. Download the application, install it and run it.
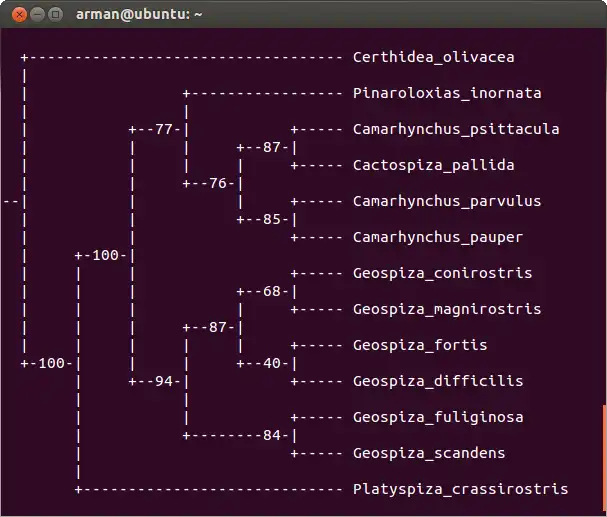
SCREENSHOTS
Ad
Javamony to run in Linux online
DESCRIPTION
Based on the not-so-successful Pysimony (https://sourceforge.net/projects/pysimony/), the same determined student takes another go at the phylogenetic problem.Javamony is invoked as follows:
java -jar Javamony.jar [input.fasta] [random / stepwise (starting tree)] [# of bootstraps] [outgroup taxon #1] [outgroup taxon #2] ...
Not meant as a competitive phylogenetic inference program, Javamony is an opportunity for me to acquire the Java language while learning to address and solve fundamental problems in phylogenetics. Therefore, for my own educational benefit, all code is original. Of course, there are probably a good deal of mistakes as well.
I distribute Javamony, as I did Pysimony, hoping that it will be of educational value to someone else or at least vaguely amusing.
Upcoming features will be:
- Support for Amino Acid sequences
- Support for additional file formats (e.g. Nexus)
- Multithreading
- Additional scoring methods (e.g. maximum likelihood)
Features
- Uses maximum parsimony
- Reads a FASTA input file (DNA only)
- User-established outgroup
- Random and stepwise-addition starting trees
- Uses SPR (subtree pruning and regrafting) tree search
- Performs bootstrapping
- Outputs standard Newick format with bootstrap support and branchlengths
- Draws final tree with bootstrap support
Audience
Science/Research, Education
User interface
Command-line
Programming Language
Java
This is an application that can also be fetched from https://sourceforge.net/projects/javamony/. It has been hosted in OnWorks in order to be run online in an easiest way from one of our free Operative Systems.