This is the Linux app named TaxOnTree whose latest release can be downloaded as TaxOnTree_v1.6.1.3_Linux_x86_64.tar.gz. It can be run online in the free hosting provider OnWorks for workstations.
Download and run online this app named TaxOnTree with OnWorks for free.
Follow these instructions in order to run this app:
- 1. Downloaded this application in your PC.
- 2. Enter in our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 3. Upload this application in such filemanager.
- 4. Start the OnWorks Linux online or Windows online emulator or MACOS online emulator from this website.
- 5. From the OnWorks Linux OS you have just started, goto our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 6. Download the application, install it and run it.
SCREENSHOTS
Ad
TaxOnTree
DESCRIPTION
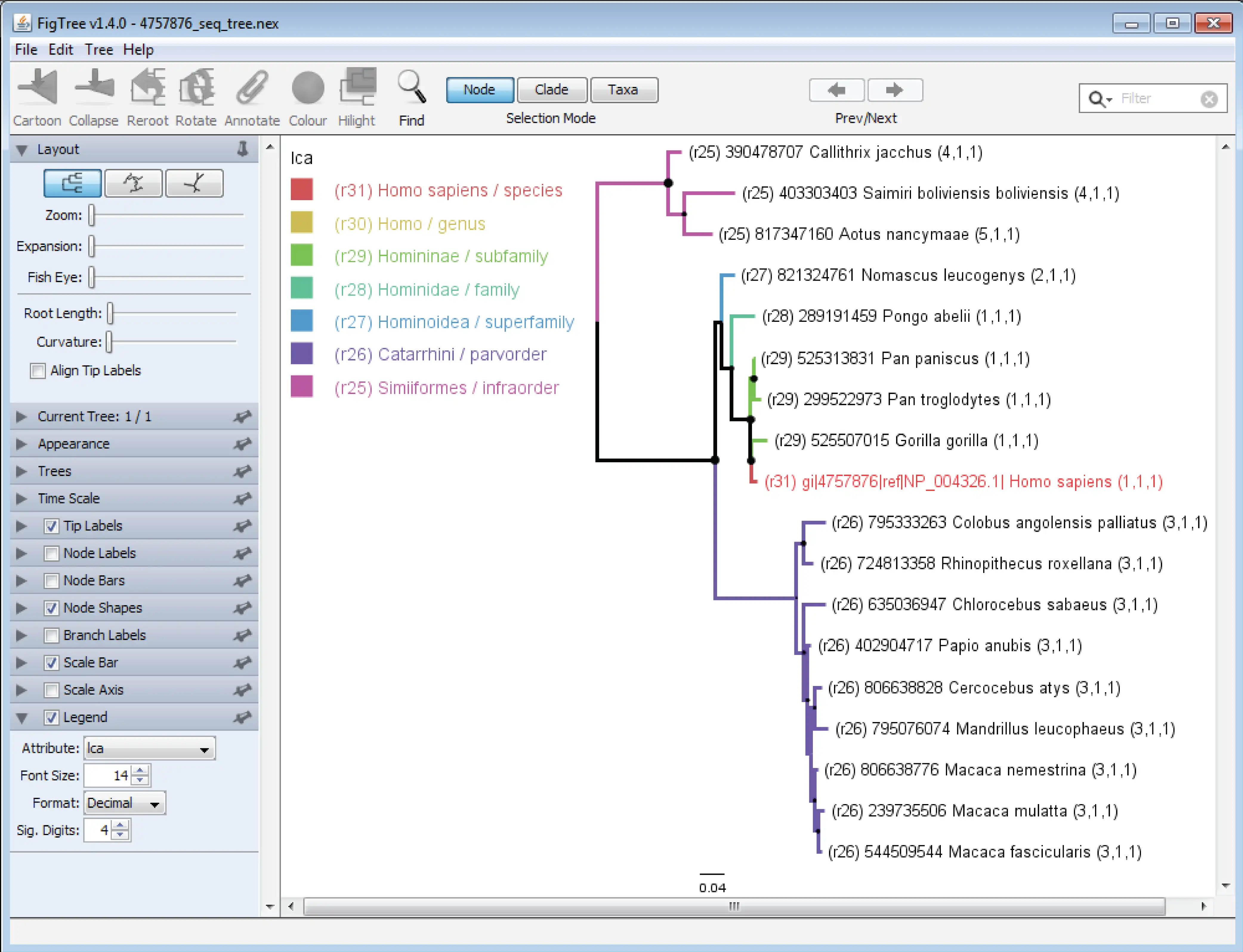
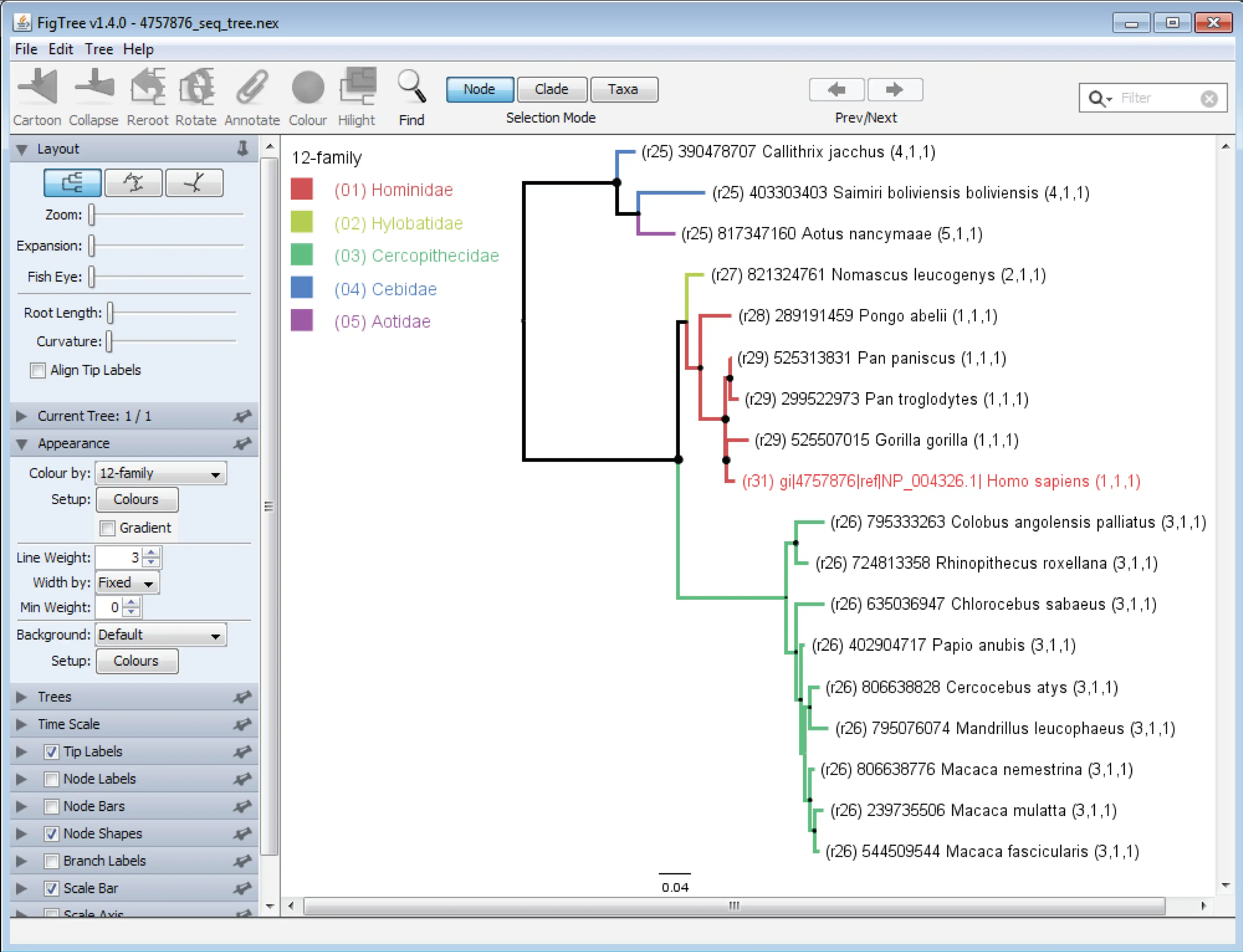
TaxOnTree is a phylogenetic program for associating Taxonomic information in a phylogenetic tree.
The output is a NEX format tree file configured to be opened in FigTree, that users can promptly color by any taxa or by the ancestrality shared by sequences with query. Input can be a Fasta formatted file to be used in a BLAST search or a list of sequences represented by their identifiers (UniProtAC or NCBI gi), if a cluster is already available. Also, a newick file produced with user software and specific settings can be used to proceed with the taxonomic labeling. TaxOnTree turns its user into an expert on taxonomy. TaxOnTree also corrects for the absence of some taxa in NCBI taxonomy. Command line program is easy to set up and can be coupled to several bioinformatics tools, producing a colored tree in PDF format. TaxOnTree is available as a web tool in http://biodados.icb.ufmg.br/taxontree for low demanding jobs.
Features
- Enter a query in fasta format (or its ID) and generate a phylogenetic tree
- RefSeq database with complete proteins only and UniProt Reference proteones are distributed with TaxOnTree
- Multiple alignment can be done with MUSCLE, PRANK, Clustal Omega or Kalign
- Alternativelly, clusters of homologues such as KO, eggNOG, OrthoMCL-DB, PANTHER, etc. can be used as input
- TaxOnTree can treat the alignment with TrimAl and builds a tree with FastTree
- However, a user built tree in newick format can be used as input for TaxOnTree
- TaxOnTree produces a NEXUS file to be opened with FigTree
- Application can run command line FigTree and export an analyzed tree in PDF
- For single usage, a web tool is available and its code is also made available for local installation
Audience
Science/Research
User interface
Command-line
Programming Language
Perl
Database Environment
Perl DBI/DBD, MySQL
Categories
This is an application that can also be fetched from https://sourceforge.net/projects/taxontree/. It has been hosted in OnWorks in order to be run online in an easiest way from one of our free Operative Systems.