This is the Linux app named EXCAVATOR-tool to run in Linux online whose latest release can be downloaded as EXCAVATOR_Package_v2.2.tgz. It can be run online in the free hosting provider OnWorks for workstations.
Download and run online this app named EXCAVATOR-tool to run in Linux online with OnWorks for free.
Follow these instructions in order to run this app:
- 1. Downloaded this application in your PC.
- 2. Enter in our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 3. Upload this application in such filemanager.
- 4. Start the OnWorks Linux online or Windows online emulator or MACOS online emulator from this website.
- 5. From the OnWorks Linux OS you have just started, goto our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 6. Download the application, install it and run it.
SCREENSHOTS
Ad
EXCAVATOR-tool to run in Linux online
DESCRIPTION
ATTENTION!!!!!ATTENTION!!!!!ATTENTION!!!!!ATTENTION!!!!!We recently published on BMC Genomics a novel software package, named XCAVATOR, for the identification of CNVs/CNAs from short and long reads whole-genome sequencing experiments (https://bmcgenomics.biomedcentral.com/articles/10.1186/s12864-017-4137-0).
XCAVATOR is freely available at http://sourceforge.net/projects/xcavator/.
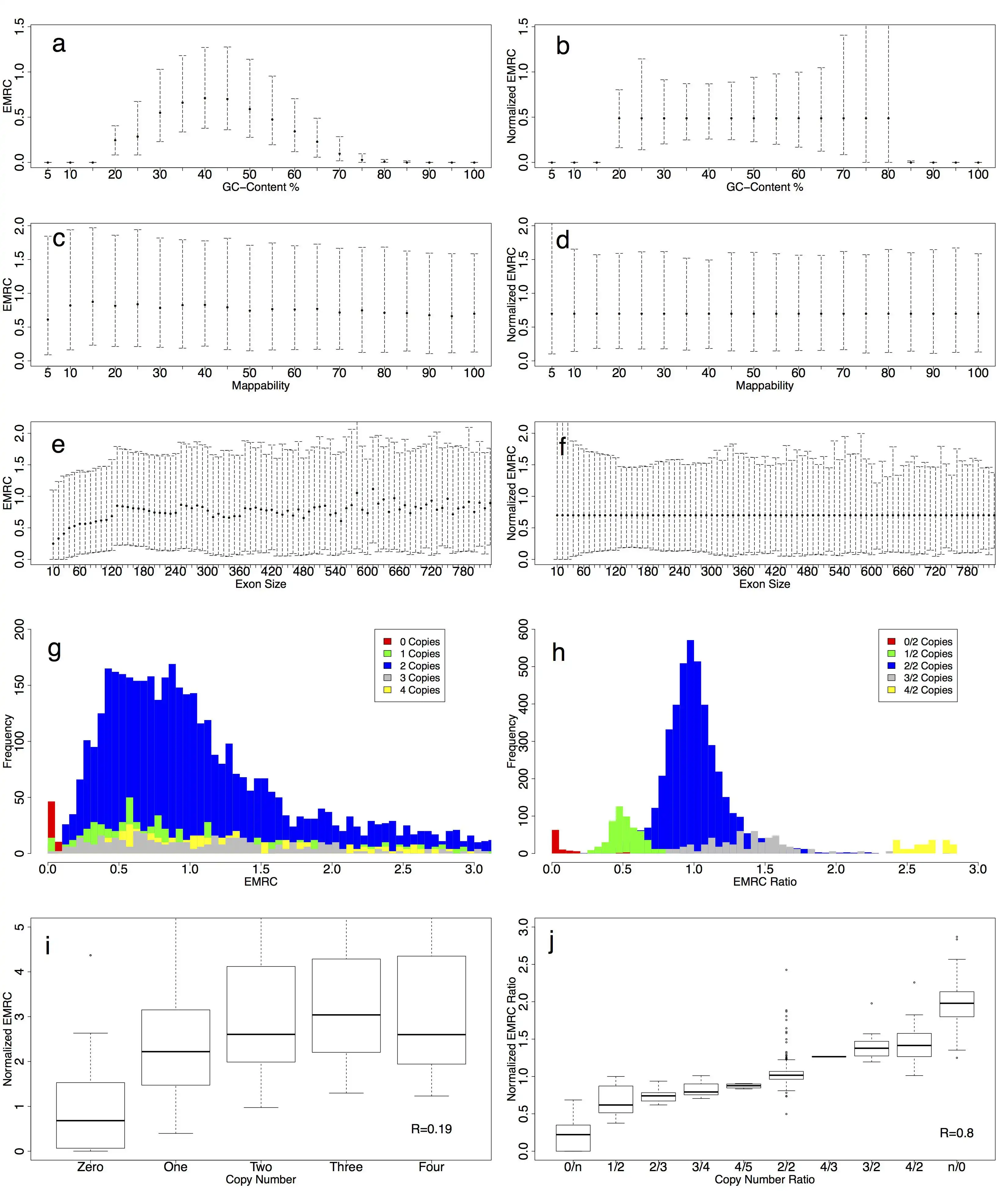
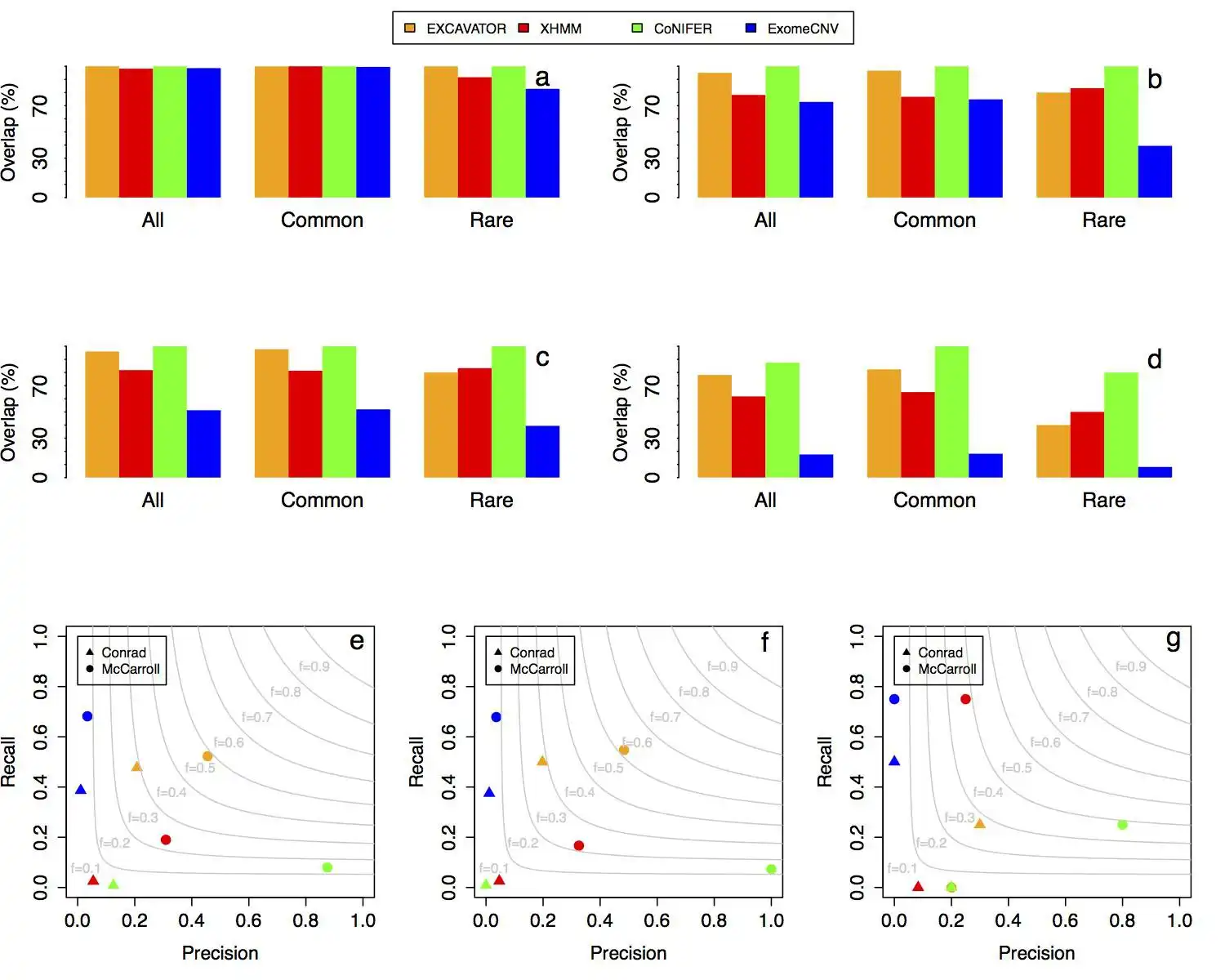
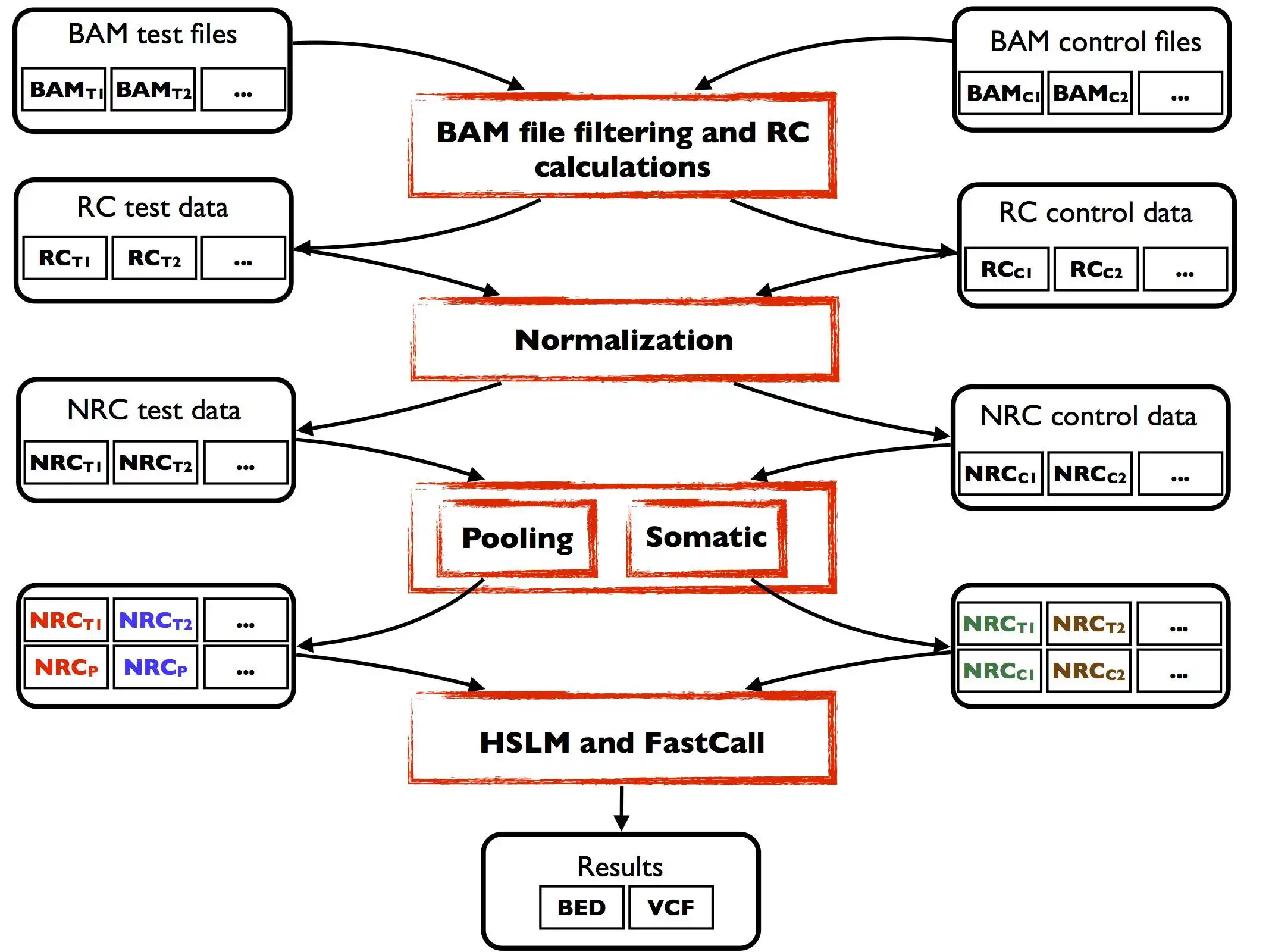
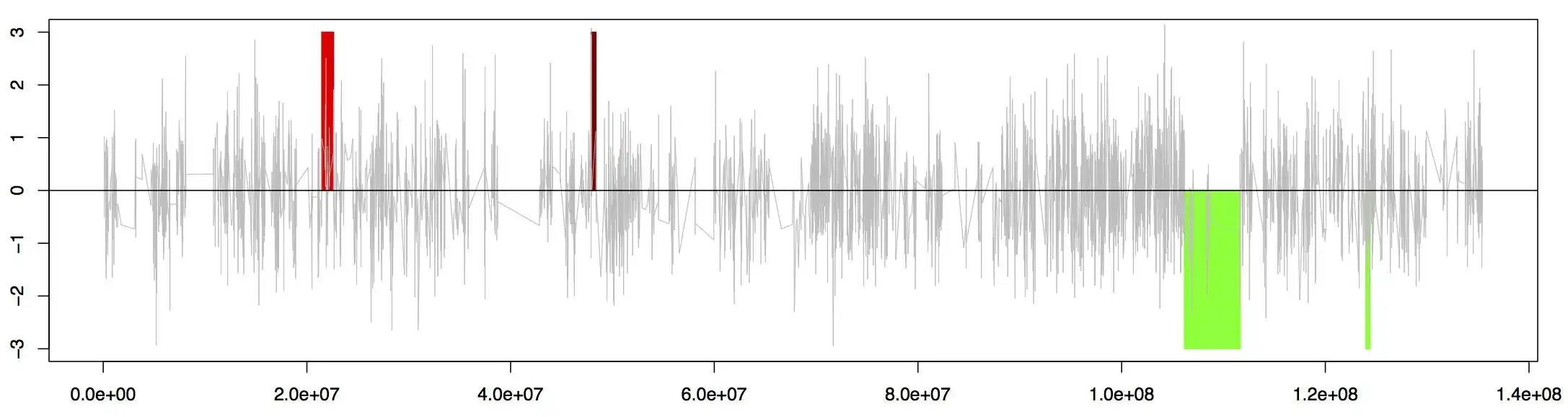
EXCAVATOR is a novel software package for the detection of copy number variants (CNVs) from whole-exome sequencing data.
EXCAVATOR has been published on Genome Biology (http://genomebiology.com/2013/14/10/R120/abstract).
####################
ATTENTION!!!!! In order to use properly the EXCAVATOR tool, users must download the uniqueome mappability files at the following link:
http://grimmond.imb.uq.edu.au/uniqueome/downloads/hg19_uniqueome.coverage.base-space.25.1.Wig.gz (for hg19)
http://grimmond.imb.uq.edu.au/uniqueome/downloads/hg18_uniqueome.coverage.base-space.25.1.Wig.gz
Features
- Next Generation Sequencing
- Copy Number Variants
- Whole Exome Sequencing
Programming Language
Perl
This is an application that can also be fetched from https://sourceforge.net/projects/excavatortool/. It has been hosted in OnWorks in order to be run online in an easiest way from one of our free Operative Systems.