This is the Linux app named UniPyRange to run in Linux online whose latest release can be downloaded as UniPyRangeSuite.py. It can be run online in the free hosting provider OnWorks for workstations.
Download and run online this app named UniPyRange to run in Linux online with OnWorks for free.
Follow these instructions in order to run this app:
- 1. Downloaded this application in your PC.
- 2. Enter in our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 3. Upload this application in such filemanager.
- 4. Start the OnWorks Linux online or Windows online emulator or MACOS online emulator from this website.
- 5. From the OnWorks Linux OS you have just started, goto our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 6. Download the application, install it and run it.
SCREENSHOTS
Ad
UniPyRange to run in Linux online
DESCRIPTION
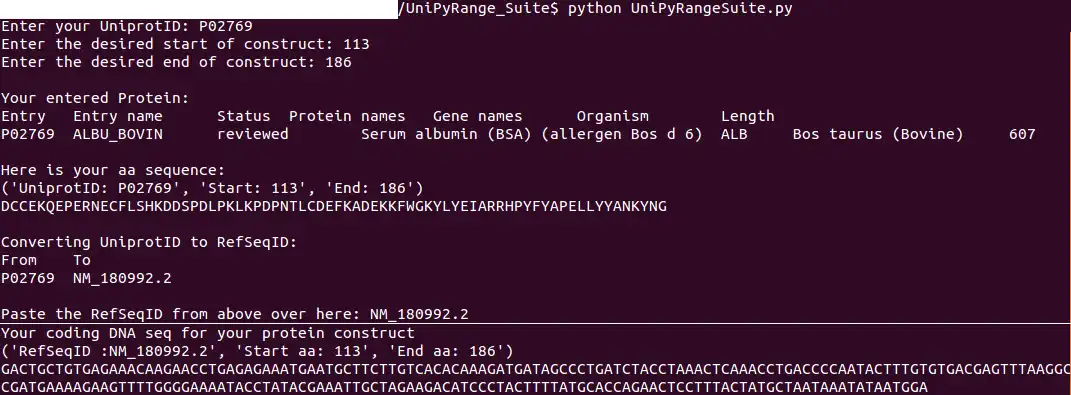
Very simple python script which saves you the pains of counting the amino acids/DNA bases in fasta files from the Uniprot and NCBI RefSeq Database (1, 2).Lets say you want the amino acid sequence of range 128-387 from a 1000 amino acid protein - this script will help you to avoid counting mistakes by just showing you the specified sequence in amino acids and coding DNA base pairs (ideal for amplification primer design) of a specified Uniprot ID.
- Requires BioPython (3) and Bioservices Package (4)
(1)
The UniProt Consortium
UniProt: a hub for protein information
Nucleic Acids Res. 43: D204-D212 (2015).
(2)
RefSeq: an update on mammalian reference sequences. Nucleic Acids Res. 2014 Jan 1;42(1):D756-63.
(3)
Cock PJ et al. Bioinformatics (2009)
(4)
Cokelaer et al, Bioinformatics (2013)
Programming Language
Python
This is an application that can also be fetched from https://sourceforge.net/projects/unipyrange/. It has been hosted in OnWorks in order to be run online in an easiest way from one of our free Operative Systems.