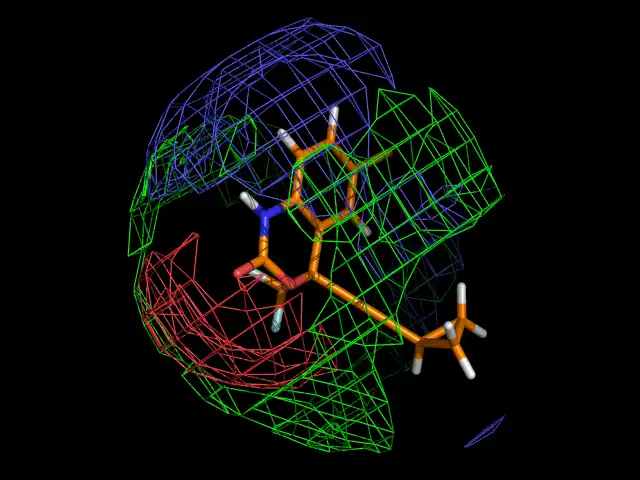
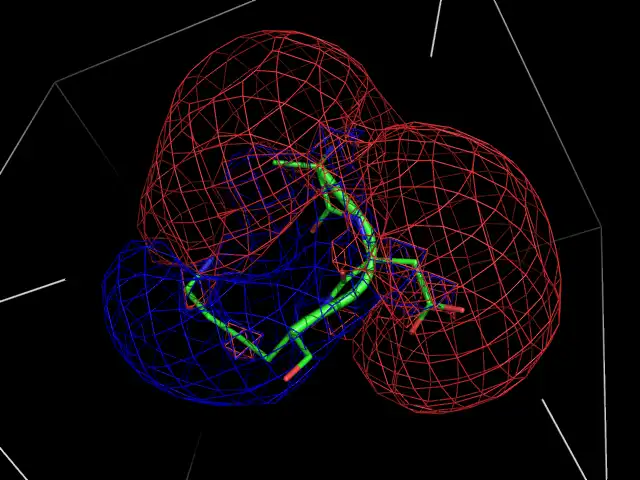
This is the Linux app named MIPGen whose latest release can be downloaded as mipgen_v15.tar.gz. It can be run online in the free hosting provider OnWorks for workstations.
Download and run online this app named MIPGen with OnWorks for free.
Follow these instructions in order to run this app:
- 1. Downloaded this application in your PC.
- 2. Enter in our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 3. Upload this application in such filemanager.
- 4. Start the OnWorks Linux online or Windows online emulator or MACOS online emulator from this website.
- 5. From the OnWorks Linux OS you have just started, goto our file manager https://www.onworks.net/myfiles.php?username=XXXXX with the username that you want.
- 6. Download the application, install it and run it.
SCREENSHOTS
Ad
MIPGen
DESCRIPTION
Molecular Interaction Potential Generator
MIPGEN is a python program that will calculate Molecular Interaction Potential grids
over a given molecule, that could be either a protein or a small organic compound (drug).
The output will be a series of grids with DX format (*.dx) that the user will be able
to visualize using any Molecular visualization program like VMD, PyMol, Chimera...
For more information on dependencies and usage, please read the Documentation.
Users are welcome to post any bug or request under BUGS & REQUESTS menu. (sourceforge account will be needed).
Features
- Fully automatic MIP generation given a simple PDB file.
- Open-source code. Users are welcome to contribute extending the probes or improving the code.
- Calculate grid based molecular interaction potentials over peptides and other macromolecular systems (probably still slow for large systems)
- Calculate MIP over small molecules
- Customizable probes. Already implemented: Hydrophobic, H-Bond donor, H-Bond acceptor and electrostatics probes.
- Automatic assignment of atom types to small molecules and proteins by interfacing with opensource Antechamber and tLeap from AmbertTools package (http://ambermd.org)
Audience
Science/Research, Advanced End Users, Developers, End Users/Desktop
User interface
Console/Terminal
Programming Language
Python
Database Environment
SQLite
Categories
This is an application that can also be fetched from https://sourceforge.net/projects/mipgen/. It has been hosted in OnWorks in order to be run online in an easiest way from one of our free Operative Systems.